XiaoMi-AI文件搜索系统
World File Search System粉末DED方法的建模技术3D金属添加剂制造机LAMDA
Ishii Hirohisa * 1 Kuramoto Hirohisa * 2 Koh Ishii Hirohisa Kuramoto Tauchi Takushi * 2 Yamamoto Yusuke * 3 Hiroyuki Tauchi Yusuke Yamamoto Wakana Tomohiro * 3 Yoshimura Jin * 3 Tomohiro Wakana Hitoshi Yoshimura
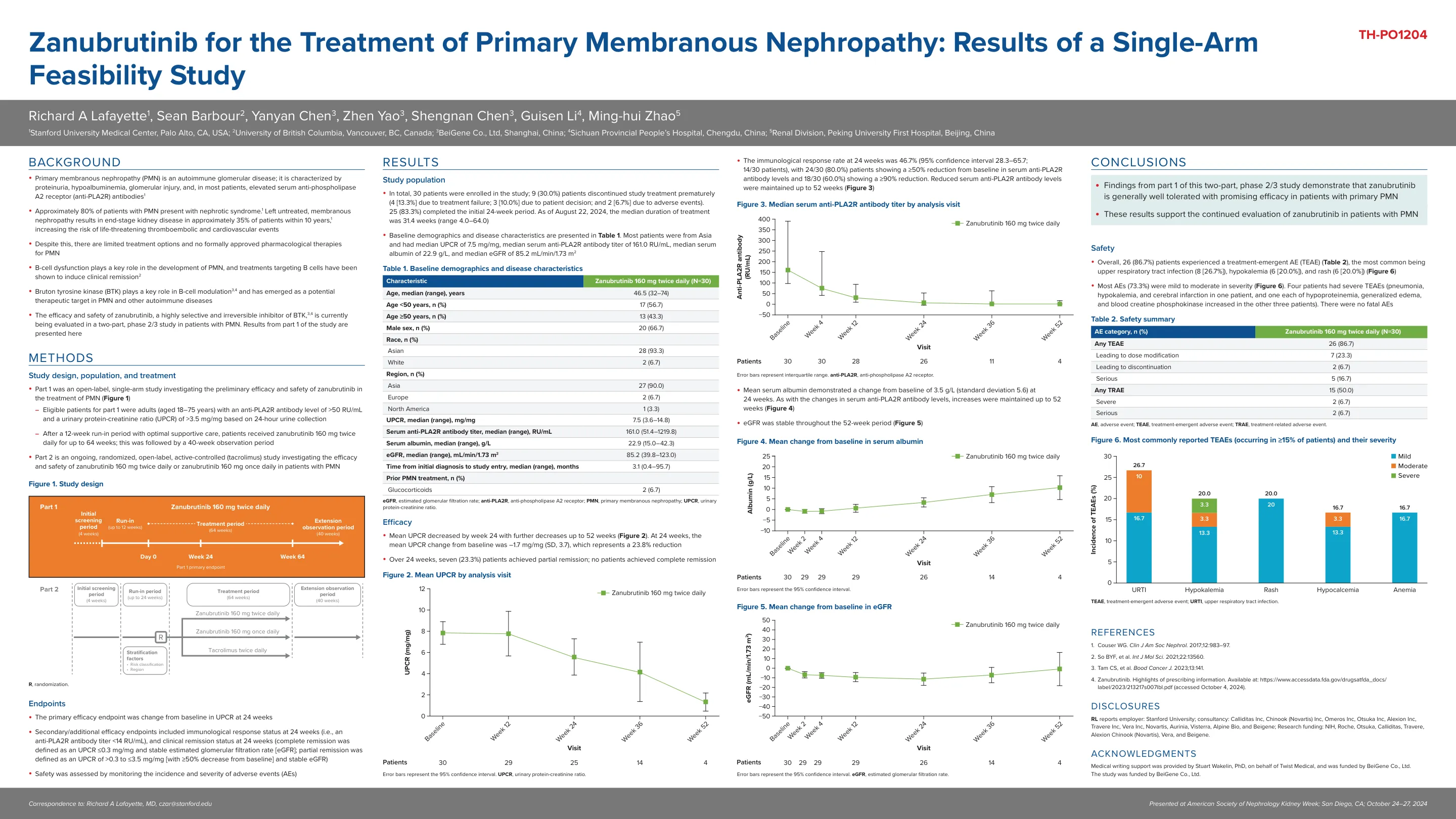
赞布替尼治疗原发性膜性肾病:单组可行性研究结果
RL 报道雇主:斯坦福大学;咨询公司:Calliditas Inc.、Chinook (Novartis) Inc.、Omeros Inc.、Otsuka Inc.、Alexion Inc.、Travere Inc.、Vera Inc.、Novartis、Aurinia、Visterra、Alpine Bio 和 Beigene;研究资金:NIH、Roche、Otsuka、Calliditas、Travere、Alexion Chinook(诺华)、Vera 和 Beigene。
活性氧引起DNA损伤的机制 还原碳水化合物...
1、CT特异性反应;2、无添加对照;3、10μg/ml CuCl2;4、20mM F-6-P和10μM CuCl2(pi
系统的元蛋白质组学映射揭示了人肠道微生物群对治疗药物的功能和生态景观
(未通过同行评审认证)是作者/资助者。保留所有权利。未经许可就不允许重复使用。此预印本版的版权持有人于2025年2月14日发布。 https://doi.org/10.1101/2025.02.13.637346 doi:Biorxiv Preprint
根据机器学习应用程序的微生物组数据的全面概述:分类,可访问性和未来方向
宏基因组学,代谢组学和元蛋白质组学通过将独立的见解与其组成和功能潜力提供了无关的见解,从而显着提高了我们对微生物群落的了解。然而,这个领域的一个关键挑战是缺乏与原始数据相关的标准和全面的元数据,从而阻碍了执行强大的数据分层并考虑混杂因素的能力。在这篇全面的综述中,我们将公开可用的微生物组数据分为五种类型:shot弹枪测序,扩增子测序,元转录组,代谢组和元蛋白质组数据。我们探讨了元数据对数据再利用的重要性,并解决了收集标准化元数据的挑战。我们还评估收集宏基因组数据的现有公共存储库的元数据收集的局限性。本综述强调了元数据在解释和比较数据集中的重要作用,并强调了对标准化元数据协议的需求,以充分利用元基因组数据的潜力。此外,我们探讨了在元数据检索中实施机器学习(ML)的未来方向,并为有前途的途径提供了对微生物群落及其生态作用的更深入了解。利用这些工具将增强我们对各种生态系统中微生物功能能力和生态动态的见解。最后,我们强调了ML模型开发中至关重要的元数据作用。
发现具有高横向热电转换性能的二维层状磁体
本研究はJSPS 科研费(JP 21H05021, JP 17H06227)、JST CREST(JPMJCR18J1)、JST SICORP
2019财年专利申请技术趋势调查(航天器)
中国空间技术研究院 (中国) 643 26,135 30 空客 (欧洲) 611 13,954 67 波音 (美国) 430 14,624 88 Energiya (俄罗斯) 430 7,401 37 三菱电机 279 89,137 20 IHI 201 13,657 28 泰雷兹 (欧洲) 153 6,495 54 三菱重工 131 27,823 16 霍尼韦尔 (美国) 117 19,431 7 雷神 (美国) 105 5,383 3 斯奈克玛 (欧洲) 102 4,363 6 太空系统/劳拉 (美国) 58 168 12 Viasat (美国) 1 685 0 蓝色起源 (美国) 12 19 1 SpaceX(美国) 1 10 9 Rocket Lab(美国) 5 5 0 北京零度空间科技公司(中国) 2 24 0 Mojave Aerospace Ventures(美国) 2 2 0 PLD space(西班牙) 0 0 0 Reaction Engines(英国) 6 13 4 Relativity Space(美国) 0 2 0 Skyrora(英国) 0 0 0 Oneweb(美国) 11 29 0 Blacksky(美国) 0 0 0 Capella Space(美国) 0 0 0 Hawkeye360(美国) 0 6 0 Iceye(芬兰) 0 1 0 OHB System(德国) 1 8 20 Planet(美国) 5 27 2 Spire Global(美国) 6 22 0 ispace(日本) 7 13 1 Planetary Resources(美国) 4 4 1 Astroscale 12 12 0 D-Orbit (意大利) 4 4 0 NASA (美国) 91 1,924 959 日本宇宙航空研究开发机构 119 500 473 国防科技大学 (中国) 69 6,274 280 哈尔滨工业大学 (中国) 338 25,237 274 加州理工学院 (美国) 19 2,648 314 韩国航空宇宙研究院 (韩国) 436 2,739 72