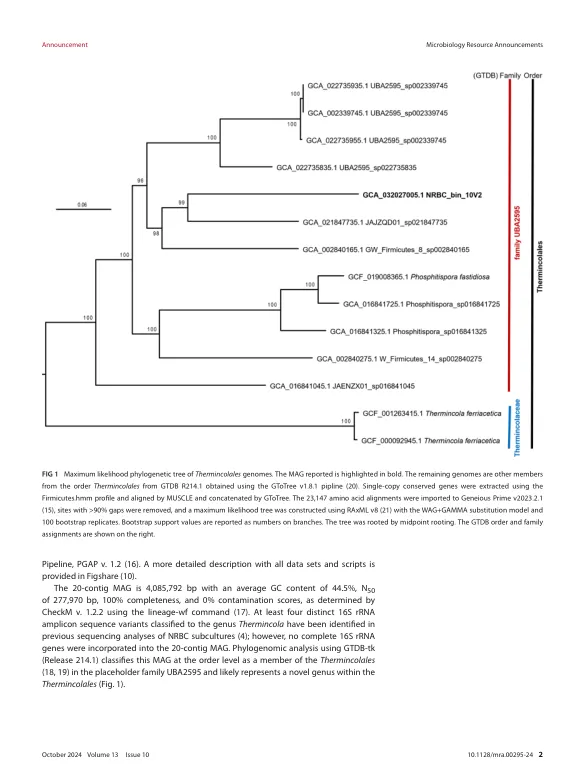
Thermincola Mag的组装使用了多个先前报道的数据集(6)。Illumina配对端(NCBI登录:SRR24043423)和Mate-pair(NCBI登录:SRR24043417)读数是从2013年从称为NRBC亚养殖Cartcons19获得的。配对末端的读数进行了测序,并使用Nextera Mate Pair库制剂制备套件对配偶对读数进行了测序。使用Trimmomaticv。0.32(7)处理所有原始读数,然后使用Abyssv。1.3.7(8),以创建与All-Paths-LGv。4.7.0(9)中生成的脚手架合并的Unitigs,使用gap填充Perl Script(10)基于Tang S1中的script in Dang et et eT eT eT eT eT eT eT eT script。(11)。由于该元基因组组装中的不确定核苷酸数量大量(JARXNP010000000),因此采取了进一步的步骤。在2018年,使用HISEQ PE群集Kit v4 cbot(Illumina)对NRBC亚培养(FES-DIASIS)进行了测序,没有其他质量控制措施(NCBI登录:SRR24043422)使用IDBAv。1.1.1.1(12)(12)和BINNENNNEND和VINNEND。在157个重叠群(NCBI登录:Javsmv000000000.1)中分配给Thermincola的垃圾箱如前所述(6)。将这157个重叠群纳入上述深渊/全paths-lg间隙填充工作流程中,生成了一个26 contig组件,该组件是通过使用BBMAPv。38.94(14)来策划映射来解决歧义的26 contig组件。读取映射可视化是使用Geneiousv。8.1.8进行的,并使用NCBI的原始基因组注释进行了基因组注释Finally, long reads from a 2020 NRBC subculture called 10L-NRBC, sequenced according to the manufac turer's instructions using PacBio RSII with the SMRTbell Express Template Prep Kit 2.0 ( SRR24043419 ) without shearing or size selection (Pacific Biosciences), were used to join adjacent contigs using the de novo assembly tool in Geneious v. 8.1.8(15),导致20碳组装。
厌氧硝酸盐还原的基因组草案,苯