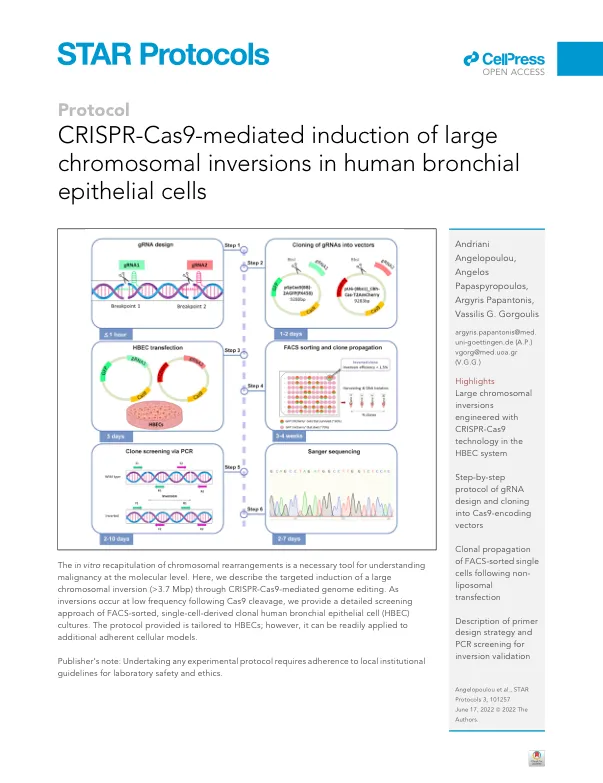
1. 通过 UCSC 基因组浏览器 ( https://genome.ucsc.edu/ ) 可获得用于设计两个 gRNA 的目标 DNA 序列。a. 选择感兴趣的基因组版本。在我们的例子中,使用的是“人类 GRCh38/hg38”。b. 根据已知的倒位断点 1 的位置,标记断点前 100-150 bp 到断点后 100–150 bp 范围内的基因组区域。例如,如果断点 1 位于 chr3:2,920,305,则在 UCSC 基因组浏览器搜索框中输入“chr3:2,920,205–2,920,405”以标记所需的染色体区域,然后单击“Go”。c. 在 UCSC 基因组浏览器工具栏上选择“查看”,然后单击“DNA”选项。d.在新窗口中,单击“获取 DNA”以获得准确的 DNA 序列。这是使用 CRISPOR 算法设计 gRNA 引物所需的序列(见下面的步骤 2a)。e. 对倒位的断点 2 重复步骤 1a-1d。2. 要设计 gRNA,请使用 CRISPOR 算法(http://crispor.tefor.net/):a. 输入从步骤 1d 获得的断点 1 的 DNA 序列。确保参考基因组与 UCSC 浏览器(步骤 1a)中使用的基因组相匹配,然后选择可通过转染载体编码的 Cas9 酶类型识别的 Protospacer Adjacent Motif (PAM)。如果转染载体表达 SpCas9,则选择 20 bp-NGG PAM 格式。单击“提交”以获得针对模板 DNA 的候选 gRNA 序列。b. CRISPOR 算法默认按特异性从高到低对候选 gRNA 序列进行排序,因为这是关键参数。从新页面上出现的候选 gRNA 列表中,选择具有最高麻省理工学院 (MIT) 和切割频率确定 (CFD) 特异性得分的指导序列(Doench 等人,2016 年;Hsu 等人,2013 年;Tycko 等人,2019 年)。这些分数根据以下方面评估候选 gRNA
CRISPR-Cas9 介导诱导人类支气管上皮细胞发生大型染色体倒位
主要关键词